Содержание
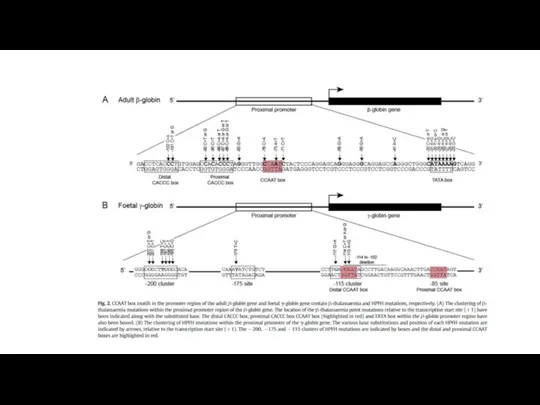
- 2. MAR Граничный элемент Энхансер -4000 Энхансер Промоторный регуляторный район -500 Ген -40 +50 Базальный или коровый
- 3. Fig. 1. Focused versus dispersed transcription initiation. In focused transcription, there is either a single major
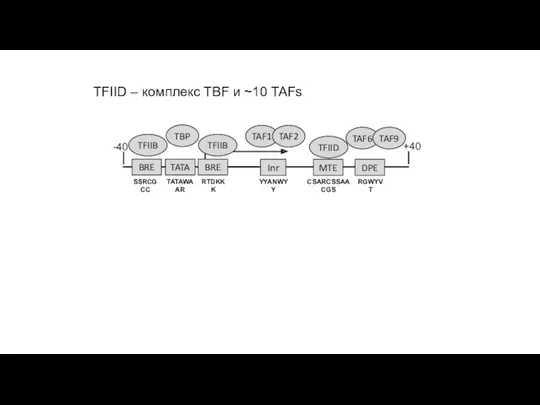
- 4. TFIID – комплекс TBF и ~10 TAFs
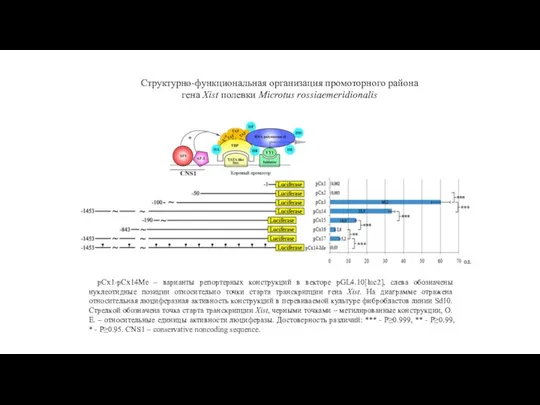
- 7. Структурно-функциональная организация промоторного района гена Xist полевки Microtus rossiaemeridionalis рСх1-рСх14Ме – варианты репортерных конструкций в векторе
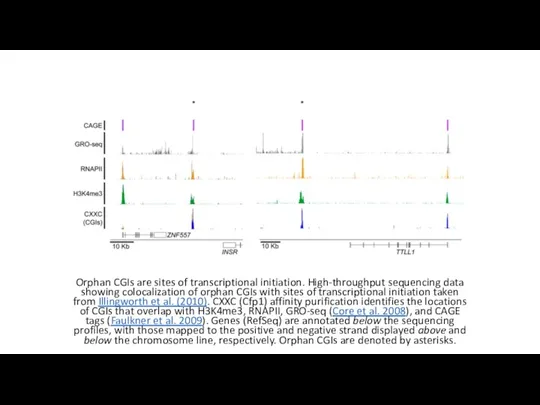
- 9. Orphan CGIs are sites of transcriptional initiation. High-throughput sequencing data showing colocalization of orphan CGIs with
- 10. Untranslated exons 1A, 1B, or 1C are spliced to the same splice acceptor site in exon
- 11. Genomic organization of mouse plectin (A), human NOS1 (B), and rat GR (C) genes. Each gene
- 12. Genome-wide distribution of human and mouse genes that have more than one first exon. The numbers
- 13. 5’ 3’ 5’ 3’ 3’ 5’ 87nt G A T C Extended primer 87 nt Free
- 14. RACE Procedure Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold Spring Harbor Laboratory Press
- 15. RNase Protection Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold Spring Harbor Laboratory Press
- 16. Интересующий промотор Репортерный ген (Люцефераза или САТ) Гетерологичный промотор Репортерный ген Для анализа промотора ИЛИ Для
- 18. Robert L. Strausberg, Elise A. Feingold, Lynette H. Grouse, Jeffery G. Derge, Richard D. Klausner, Francis
- 19. mRNA mRNA mRNA mRNA mRNA mRNA mRNA mRNA mRNA mRNA mRNA mRNA
- 21. The eukaryotic promoter database in its 30th year: focus on non-vertebrate organisms. Dreos R., Ambrosini G.,
- 22. CAGE
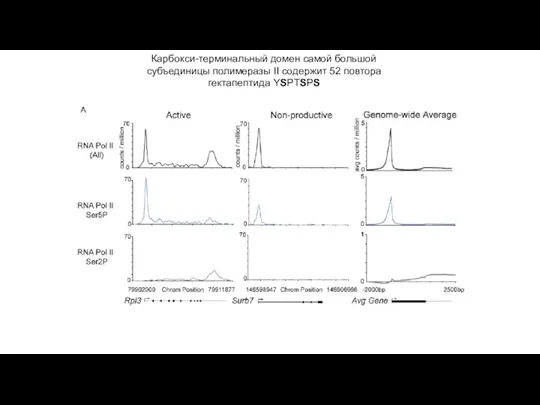
- 28. Карбокcи-терминальный домен самой большой субъединицы полимеразы II содержит 52 повтора гектапептида YSPTSPS
- 31. ENCODE Project Scientific Management: National Human Genome Research Institute (E. A. Feingold, P. J. Good, M.
- 32. The ENCODE Project Consortium. 2004. The ENCODE (ENCyclopedia Of DNA Elements) Project. Science 306: 636–640. Functional
- 33. Интересующий промотор Репортерный ген (Люцефераза или САТ) Гетерологичный промотор Репортерный ген Для анализа промотора ИЛИ Для
- 35. Скачать презентацию
MAR
Граничный
элемент
Энхансер
-4000
Энхансер
Промоторный регуляторный район
-500
Ген
-40
+50
Базальный или коровый
промотор
Граничный
элемент
MAR
Инициаторный комплекс
Pol II
Mediator
IIH
USA
IIA
TBP
TAFs
IIB
IIF
CBP
IIE
Transcriptional Regulation in Eukaryotes:
MAR
Граничный
элемент
Энхансер
-4000
Энхансер
Промоторный регуляторный район
-500
Ген
-40
+50
Базальный или коровый
промотор
Граничный
элемент
MAR
Инициаторный комплекс
Pol II
Mediator
IIH
USA
IIA
TBP
TAFs
IIB
IIF
CBP
IIE
Transcriptional Regulation in Eukaryotes:
Fig. 1.
Focused versus dispersed transcription initiation. In focused transcription, there is
Fig. 1.
Focused versus dispersed transcription initiation. In focused transcription, there is
TFIID – комплекс TBF и ~10 TAFs
TFIID – комплекс TBF и ~10 TAFs
Структурно-функциональная организация промоторного района гена Xist полевки Microtus rossiaemeridionalis
рСх1-рСх14Ме –
Структурно-функциональная организация промоторного района гена Xist полевки Microtus rossiaemeridionalis
рСх1-рСх14Ме –
Orphan CGIs are sites of transcriptional initiation. High-throughput sequencing data showing
Orphan CGIs are sites of transcriptional initiation. High-throughput sequencing data showing
Untranslated exons 1A, 1B, or 1C are spliced to the same
Untranslated exons 1A, 1B, or 1C are spliced to the same
Diagram of the hGR Gene Structure
and Organization
Genomic organization of mouse plectin (A), human NOS1 (B), and rat
Genomic organization of mouse plectin (A), human NOS1 (B), and rat
Each gene contains a tandem array of multiple first exons in the variable region, each of which is separately spliced to a common set of downstream constant exons.The approximate length of each gene is shown below the corresponding panels.
Theresa Zhang, Peter Haws and Qiang Wu. Multiple Variable First Exons: A Mechanism for Cell- andTissue-Specific Gene Regulation. 2004 14: 79-89; Genome Res.
Множественные экзоны 1
Genome-wide distribution of human and mouse genes that have more than
Genome-wide distribution of human and mouse genes that have more than
The numbers are shown above each histogram.The inset shows an enlargement of the distribution of genes with more than three first exons.
Theresa Zhang, Peter Haws and Qiang Wu. Multiple Variable First Exons: A Mechanism for Cell- andTissue-Specific Gene Regulation. 2004 14: 79-89; Genome Res.
Множественные экзоны 1
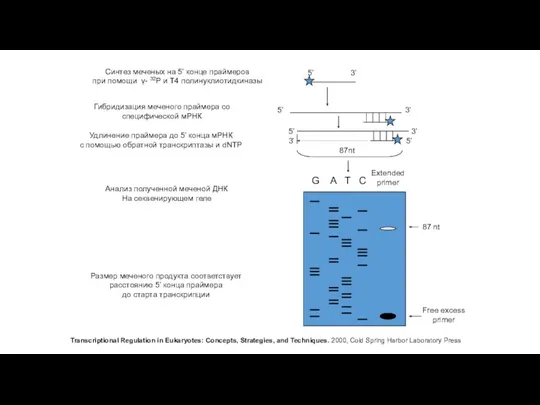
5’ 3’
5’
3’
3’
5’
87nt
G A T C
Extended
primer
87 nt
Free excess
primer
Синтез меченых на 5’ конце
5’ 3’
5’
3’
3’
5’
87nt
G A T C
Extended
primer
87 nt
Free excess
primer
Синтез меченых на 5’ конце
при помощи γ- 32P и Т4 полинуклиотидкиназы
Гибридизация меченого праймера со
специфической мРНК
5’
3’
Удлинение праймера до 5’ конца мРНК
c помощью обратной транскриптазы и dNTP
Анализ полученной меченой ДНК
На секвенирующем геле
Размер меченого продукта соответствует
расстоянию 5’ конца праймера
до старта транскрипции
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold Spring Harbor Laboratory Press
RACE Procedure
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold
RACE Procedure
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold
Hybridize primer 100–200 nucleotides from 5′ end of mRNA.
Extend primer to 5′ end of mRNA using reverse transcriptase
and dNTPs.
Ligate oligo of known sequence to 3′ end of cDNA using RNA
ligase. Alternatively, extend cDNA using terminal transferase
(TdT) and dGTP.
Perform PCR using primer complementary to ligated oligo and a downstream primer that is slightly internal to the primer used for
cDNA synthesis above.
(Optional)
Sequence PCR products
Sequence
Individual clones
Determine size on
sequencing gel (if
radiolabeled primer
used for PCR).
Insert PCR
product into
vector
RNase Protection
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold
RNase Protection
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold
Plasmid includes region of gene containing
putativetranscription start site and 59 nucleotides
downstreamof this start site, fused to the SP6
promoter and flanked by convenient restriction sites.
Cut with HindIII to linearize plasmid.
Add transcription buffer, SP6 RNA polymerase, NTPs plus [α -32P]UTP (asterisks) to generate antisense probe.
Hybridize probe to isolated mRNA.
Digest with RNase T1 and RNase A
(cleaves single-stranded RNAs).
Creates a 59-nucleotide RNA-RNA hybrid.
Denature and analyze by denaturing gel electrophoresis.
Интересующий промотор
Репортерный ген
(Люцефераза или САТ)
Гетерологичный промотор
Репортерный
ген
Для анализа промотора
ИЛИ
Для анализа
Интересующий промотор
Репортерный ген
(Люцефераза или САТ)
Гетерологичный промотор
Репортерный
ген
Для анализа промотора
ИЛИ
Для анализа
регуляторного района
отдаленный
регуляторный район
Трансфекция клеток
репортерной плазмидой
Инкубация в течении 24-72 часов
транскрипция для эписомных плазмид и
синтез белка
Измерение
активности
фермента
репортерного гена
Измерение уровня
репортерной мРНК
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold Spring Harbor Laboratory Press
Методы исследования регуляторных районов
Robert L. Strausberg, Elise A. Feingold, Lynette H. Grouse, Jeffery G. Derge, Richard D. Klausner, Francis
Robert L. Strausberg, Elise A. Feingold, Lynette H. Grouse, Jeffery G. Derge, Richard D. Klausner, Francis
Contributed by Francis S. Collins, et al.
Generation and initial analysis of more than 15,000 full-length human and mouse cDNA sequences
Mammalian Gene Collection (MGC) Program Team*, 2000.
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
mRNA
The eukaryotic promoter database in its 30th year:
focus on non-vertebrate
The eukaryotic promoter database in its 30th year:
focus on non-vertebrate
Dreos R., Ambrosini G., Groux R., Cavin Périer R., Bucher P.
Nucleic Acids Res. 2017 Jan 4;45(D1):D51-D55. doi: 10.1093/nar/gkw1069. Epub 2016 Nov 28.
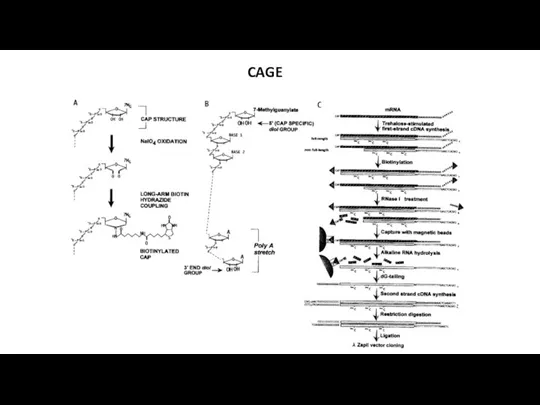
CAGE
CAGE
Карбокcи-терминальный домен самой большой субъединицы полимеразы II содержит 52 повтора гектапептида
Карбокcи-терминальный домен самой большой субъединицы полимеразы II содержит 52 повтора гектапептида
ENCODE Project Scientific Management:
National Human Genome Research Institute (E. A.
Feingold, P.
ENCODE Project Scientific Management:
National Human Genome Research Institute (E. A.
Feingold, P.
K. Wetterstrand, F. S. Collins).
Initial ENCODE Pilot Phase Participants:
Affymetrix, Inc. (T. R. Gingeras, D. Kampa, E. A. Sekinger,
J. Cheng, H. Hirsch, S. Ghosh, Z. Zhu, S. Patel, A. Piccolboni, A. Yang, H. Tammana, S. Bekiranov, P. Kapranov, R. Harrison, G. Church, K. Struhl); Ludwig Institute for Cancer Research (B. Ren, T. H. Kim, L. O. Barrera, C. Qu, S. Van Calcar, R. Luna, C. K. Glass, M. G. Rosenfeld); Municipal Institute of Medical Research (R. Guigo, S. E. Antonarakis, E. Birney, M. Brent, L. Pachter, A. Reymond, E. T. Dermitzakis, C. Dewey, D. Keefe, F. Denoeud, J. Lagarde, J. Ashurst, T. Hubbard, J. J. Wesselink, R. Castelo, E. Eyras); Stanford University (R. M. Myers, A. Sidow, S. Batzoglou, N. D. Trinklein, S. J. Hartman, S. F. Aldred, E. Anton, D. I. Schroeder, S. S. Marticke, L. Nguyen, J.Schmutz, J.Grimwood,M.Dickson, G. M. Cooper, E. A. Stone, G. Asimenos, M. Brudno); University of Virginia (A. Dutta, N. Karnani, C. M. Taylor, H. K. Kim, G. Robins); University of Washington (G. Stamatoyannopoulos, J. A. Stamatoyannopoulos, M. Dorschner, P. Sabo, M. Hawrylycz, R. Humbert, J. Wallace, M. Yu, P. A. Navas, M. McArthur, W. S. Noble); Wellcome Trust Sanger Institute (I. Dunham, C. M. Koch, R.M.Andrews,G. K.Clelland, S. Wilcox, J. C. Fowler, K.D.
James, P. Groth, O. M. Dovey, P. D. Ellis, V. L. Wraight, A. J. Mungall, P. Dhami, H. Fiegler, C. F. Langford, N. P. Carter,
D. Vetrie); Yale University (M. Snyder, G. Euskirchen, A. E.
Urban, U. Nagalakshmi, J. Rinn, G. Popescu, P. Bertone, S.
Hartman, J. Rozowsky, O. Emanuelsson, T. Royce, S. Chung, M. Gerstein, Z. Lian, J. Lian, Y. Nakayama, S. Weissman, V. Stolc, W. Tongprasit, H. Sethi).
Additional ENCODE Pilot Phase Participants:
British Columbia Cancer Agency Genome Sciences Centre (S. Jones, M. Marra, H. Shin, J. Schein); Broad Institute (M. Clamp, K. Lindblad-Toh, J. Chang, D. B. Jaffe, M. Kamal, E. S. Lander, T. S. Mikkelsen, J. Vinson, M. C. Zody); Children’s Hospital Oakland Research Institute
(P. J. de Jong, K. Osoegawa,M.Nefedov, B. Zhu); National Human Genome Research Institute/Computational Genomics Unit (A. D. Baxevanis, T. G. Wolfsberg); National Human Genome Research Institute/Molecular Genetics Section (F. S. Collins, G. E. Crawford, J. Whittle, I. E. Holt, T. J. Vasicek, D. Zhou, S. Luo); NIH Intramural
Sequencing Center/National Human Genome Research Institute (E. D. Green, G. G. Bouffard, E. H. Margulies, M. E. Portnoy, N. F. Hansen, P. J. Thomas, J. C. McDowell, B. Maskeri, A. C. Young, J. R. Idol, R. W. Blakesley); National Library of Medicine (G. Schuler); Pennsylvania State University (W. Miller, R. Hardison, L. Elnitski, P. Shah); The Institute for Genomic Research (S. L. Salzberg, M. Pertea, W. H. Majoros); University of California, Santa Cruz (D. Haussler, D. Thomas, K. R. Rosenbloom, H. Clawson, A. Siepel, W. J. Kent).
ENCODE Technology Development Phase Participants:
Boston University (Z. Weng, S. Jin, A. Halees, H. Burden, U. Karaoz, Y. Fu, Y. Yu, C. Ding, C. R. Cantor); Massachusetts General Hospital (R. E. Kingston, J. Dennis); NimbleGen Systems, Inc. (R. D. Green,M. A. Singer, T. A. Richmond, J. E. Norton, P. J Farnham, M. J. Oberley, D. R. Inman); NimbleGen Systems, Inc. (M. R. McCormick, H. Kim, C. L. Middle, M. C. Pirrung); University of California, et al!
The ENCODE Project Consortium. 2004. The ENCODE (ENCyclopedia Of DNA Elements) Project. Science 306: 636–640.
The ENCODE Project Consortium
The ENCODE Project Consortium. 2004. The ENCODE (ENCyclopedia Of DNA Elements)
The ENCODE Project Consortium. 2004. The ENCODE (ENCyclopedia Of DNA Elements)
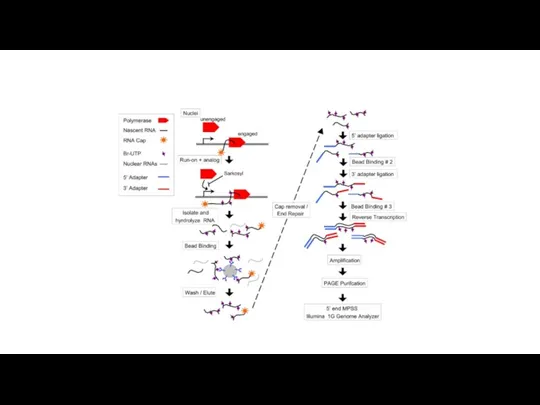
Functional genomic elements being identified by the ENCODE pilot phase.
The indicated methods are being used to identify different types of
functional elements in the human genome
Интересующий промотор
Репортерный ген
(Люцефераза или САТ)
Гетерологичный промотор
Репортерный
ген
Для анализа промотора
ИЛИ
Для анализа
Интересующий промотор
Репортерный ген
(Люцефераза или САТ)
Гетерологичный промотор
Репортерный
ген
Для анализа промотора
ИЛИ
Для анализа
регуляторного района
отдаленный
регуляторный район
Трансфекция клеток
репортерной плазмидой
Инкубация в течении 24-72 часов
транскрипция для эписомных плазмид и
синтез белка
Измерение
активности
фермента
репортерного гена
Измерение уровня
репортерной мРНК
Transcriptional Regulation in Eukaryotes: Concepts, Strategies, and Techniques. 2000, Cold Spring Harbor Laboratory Press
Методы исследования регуляторных районов














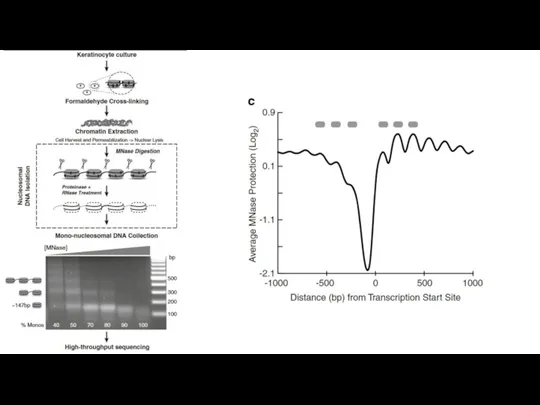

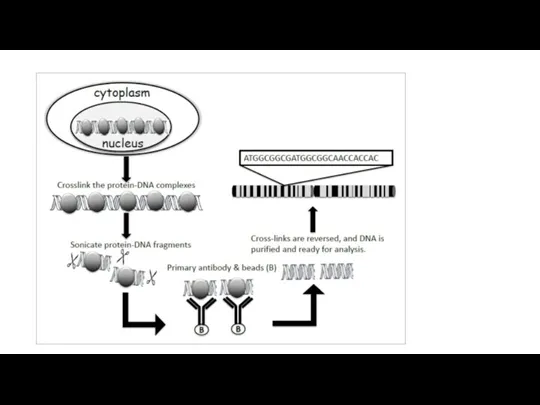


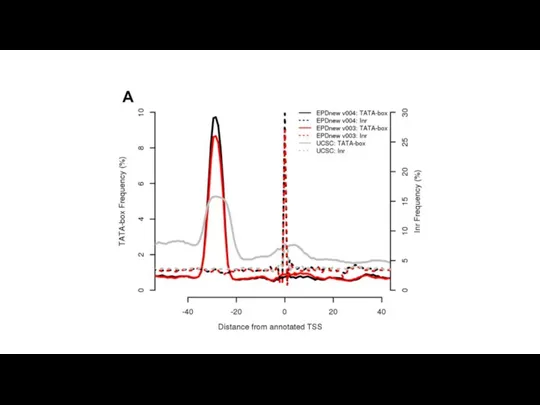


 Органи дихання людини
Органи дихання людини Актинидия. Особенности
Актинидия. Особенности Здоровый сад – основные правила и типичные ошибки
Здоровый сад – основные правила и типичные ошибки Значення бульбочкових бактерій у сільському господарстві
Значення бульбочкових бактерій у сільському господарстві Скелетные мышцы. Физиология возбудимых тканей
Скелетные мышцы. Физиология возбудимых тканей Как разные животные готовятся к зиме
Как разные животные готовятся к зиме Генетика. Наследственность. Изменчивость
Генетика. Наследственность. Изменчивость Тип членистоногие (arthropoda)
Тип членистоногие (arthropoda) Царство грибы
Царство грибы Тип Кишечнополостные
Тип Кишечнополостные Основы морфологии растений
Основы морфологии растений презентация к уроку биологии 7 класс
презентация к уроку биологии 7 класс Кубанские умельцы
Кубанские умельцы Презентация к внеклассному мероприятию Биология в профессиях
Презентация к внеклассному мероприятию Биология в профессиях Общие принципы организации тканей. Эпителиальные ткани
Общие принципы организации тканей. Эпителиальные ткани Ферментные препараты, используемые в молочной промышленности
Ферментные препараты, используемые в молочной промышленности Тонкая кишка
Тонкая кишка Деление клетки. Митоз
Деление клетки. Митоз Почвы горных областей Казахстана
Почвы горных областей Казахстана Сибиоз. Лишайники
Сибиоз. Лишайники Селекция. Современные методы селекции
Селекция. Современные методы селекции Митохондрии. Строение, функции, происхождение митохондрий
Митохондрии. Строение, функции, происхождение митохондрий Систематика пресмыкающихся
Систематика пресмыкающихся Зрительный анализатор. Анатомия и физиология глаза
Зрительный анализатор. Анатомия и физиология глаза Физиология сосудов. (Лекция 5.2)
Физиология сосудов. (Лекция 5.2) Мужская половая система
Мужская половая система Красная книга. Животные
Красная книга. Животные Селекция животных
Селекция животных